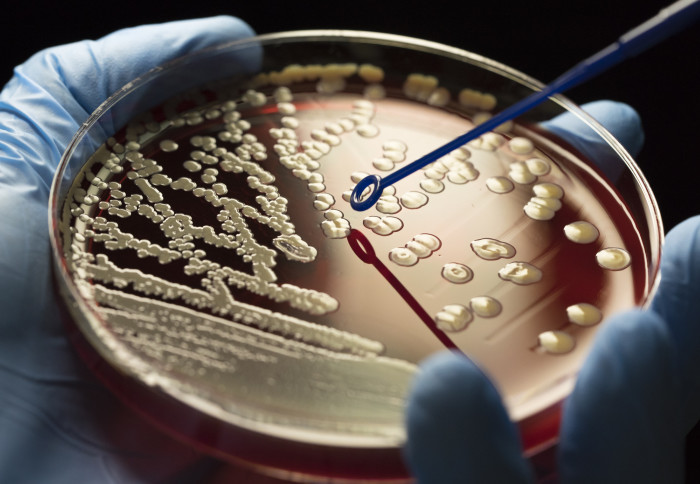
محققان اطلاعات ارزشمندی درخصوص عواملی ارائه کردهاند که باعث گسترش جهانی ژنهای مسئول مقاومت باکتریها در برابر آنتیبیوتیکها میشود.
به گزارش آماج از وبگاه فیز (phys)، یک تیم پژوهشی بینالمللی، اطلاعات ارزشمند جدیدی درباره عواملی ارائه کردهاند که باعث گسترش جهانی ژنهای مسئول مقاومت در برابر آنتیبیوتیک (AMR) در باکتریها میشود.
در این پژوهش مشترک، که به سرپرستی محققان مؤسسه کوادرَم در انگلیس و دانشگاه شرق انگلستان انجام شده است، محققانی از فرانسه، کانادا، آلمان و انگلیس گرد هم آمدهاند و اطلاعات جدیدی را برای مبارزه با مشکل جهانی مقاومت در برابر آنتیبیوتیک ارائه کردهاند.
تیم پژوهشی با توالییابی کل ژنوم حدود ۲ هزار باکتری مقاوم، از جمله اِشریشیا کُلی، که بین سالهای ۲۰۰۸ و ۲۰۱۶ جمعآوری شدهاند، دریافتند که دینامیک زمانی انواع مختلف ژنهای مقاوم در برابر آنتیبیوتیک متفاوت است؛ مثلاً برخی از آنها ابتدا در آمریکای شمالی یافت شدند و به اروپا گسترش یافتند، در حالی که برخی دیگر از اروپا به آمریکای شمالی گسترش یافتند.
محققان فقط به بررسی باکتریهایی از مناطق مختلف جغرافیایی بسنده نکردند؛ بلکه میزبانهای متنوعی از جمله انسان، حیوانات، غذا (گوشت) و محیط (فاضلاب) را نیز تجزیهوتحلیل کردند تا مشخص کنند چگونه این عوامل مجزا اما به هم پیوسته بر توسعه و گسترش مقاومت در برابر آنتیبیوتیک تأثیر گذاشتهاند.
محققان بر روی مقاومت به یک گروه خاص از ضدمیکروبیها، یعنی سفالوسپورینهای طیف گسترده (ESCs)، تمرکز کردند. سازمان بهداشت جهانی این ضدمیکروبیها را بهعنوان بسیار مهم طبقهبندی کرده است؛ زیرا آنها آخرین راهحل برای درمان باکتریهای مقاوم به چند دارو بهشمار میروند؛ هرچند، از زمان معرفی آنها، اثربخشیشان کاهش یافته است؛ زیرا باکتریها مقاومت ایجاد کردهاند.
باکتریهایی که به سفالوسپورینهای طیف گسترده مقاوم هستند از طریق تولید آنزیمهای خاصی به نام بتالاکتاماز که قادر به غیرفعال کردن سفالوسپورینهای طیف گسترده هستند، به این هدف میرسند. دستورالعملهای ساخت این آنزیمها در ژنها، بهویژه دو نوع ژن اصلی، رمزگذاری شدهاند: بتالاکتامازهای طیف گسترده (ESBLs)، و بتالاکتامازهای نوع AmpC (AmpCs).
این ژنها ممکن است در کروموزومهای باکتری یافت شوند؛ یعنی جایی که طی تکثیر کلونال یا در پلاسمیدها (مولکولهای کوچک دیاِناِی جدا از کروموزوم اصلی باکتری) به فرزندان منتقل میشوند. پلاسمیدها متحرک هستند و میتوانند به صورت مستقیم، بین باکتریهای منفرد حرکت کنند که نشاندهنده یک راه جایگزین برای تبادل مواد ژنتیکی است.
این پژوهش نشان داد که چگونه برخی از ژنهای مقاومت در برابر آنتیبیوتیک، از طریق گسترش کلونال زیرگروههای باکتریایی تکثیر میشوند؛ در حالی که برخی دیگر به طور مستقیم بر روی پلاسمیدهای همهگیری به میزبانها و کشورهای مختلف منتقل میشوند.
فهمیدن جریان اطلاعات ژنتیکی درون و بین جمعیتهای باکتریایی برای فهم انتقال مقاومت در برابر آنتیبیوتیک و گسترش جهانی آن اهمیت ویژه دارد. این دانش به طراحی مداخلات حیاتی لازم کمک میکند که میتواند مقاومت در برابر آنتیبیوتیک را در دنیای واقعی متوقف کند؛ دنیای واقعی جایی است که باکتریهای میزبانها و جایگاههای محیطی مختلف در تعامل هستند و سفر و تجارت بینالمللی به این معنا است که جغرافیا این تعاملات را محدود نمیکند.
پروفسور آلیسون مَتِر (Alison Mather)، سرپرست پژوهش، گفت: با گردآوری این مجموعه وسیع و متنوع از ژنومها، توانستیم ژنهای اصلی تولیدکننده مقاومت در برابر این داروهای بسیار مهم را شناسایی کنیم؛ همچنین متوجه شدیم که تعداد محدودی از پلاسمیدهای غالب و رده باکتریایی، بیشترین مقاومت به سفالوسپورینهای طیف گسترده را پخش میکنند؛ درک سازوکارهای (مکانیسمهای) انتقال برای طراحی مداخلات بهمنظور کاهش انتشار مقاومت در برابر آنتیبیوتیک بسیار مهم است.
به گفته محققان، مقاومت ضدمیکروبی یک مشکل جهانی است و فقط با همکاری مشترک با چندین کشور میتوان درک جامعی از مکان و نحوه انتشار مقاومت در برابر آنتیبیوتیک بهدست آورد.